Qunova HiVQEによる解離ポテンシャルエネルギー曲面の計算
Qiskit Functionsは、IBM Quantum® Premium Plan、Flex Plan、およびOn-Prem(IBM Quantum Platform API経由)Planのユーザーのみが利用できる実験的な機能です。プレビューリリースの状態であり、変更される可能性があります。
使用量の見積もり(注意:これは見積もりです。実際の実行時間は異なる場合があります。)
- Li2S:Heron r2プロセッサでのQPU時間 約5分
- FeP-NO:Heron r2プロセッサでのQPU時間 約5分
背景
化学反応エネルギーの正確な計算は、材料科学、化学工学、創薬、その他の分野における科学的進歩にとって極めて重要です。様々な化学系の中でも、Li-S系は新しいバッテリー組成の理解と開発において大きな関心を集めています。このチュートリアルでは、HiVQE計算を用いて、系からリチウム原子を1つ除去する際のLi-S結合解離ポテンシャルエネルギー曲面(PES)を計算する実践的な経験を提供します。結果は、参照計算(CASCI)およびHartree-Fock(HF)などの古典的手法と、20量子ビット問題として比較することができます。
要件
このチュートリアルのコードを実行するには、以下の依存関係をインストールしてください。
!pip install --upgrade pip
!pip install -U qiskit-ibm-catalog "qiskit_ibm_runtime<0.42.0" pyscf numpy matplotlib typing_extensions
セットアップ
このチュートリアルを実行するには、QiskitFunctionCatalogを通じてqunova/hivqe-chemistry関数をインポートします。この関数を実行するには、IBM Quantum Premium Plan、Flex Plan、またはOn-Prem(IBM Quantum Platform API)Planのアカウントと、Qunovaからのライセンスが必要です。
from qiskit_ibm_catalog import QiskitFunctionsCatalog
from pyscf import gto, scf, mcscf
import matplotlib.pyplot as plt
import pprint
catalog = QiskitFunctionsCatalog(
channel="ibm_quantum_platform",
instance="INSTANCE_CRN",
token="YOUR_API_KEY", # Use the 44-character API_KEY you created and saved from the IBM Quantum Platform Home dashboard
)
hivqe = catalog.load("qunova/hivqe-chemistry")
パート1:Li2S(20量子ビット)
ステップ1:古典的な入力を量子問題にマッピングする
PES曲線を計算するために、Li-Sの異なる結合距離に対するのジオメトリを辞書形式で定義します。これらのジオメトリはB3LYP/631g計算を用いて最適化されています。
str_geometries = {
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
str_geometries
{'1.51': 'S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768',
'1.91': 'S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257',
'2.40': 'S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209',
'3.10': 'S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522',
'3.80': 'S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063',
'4.50': 'S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670'}
HiVQE計算は以下に定義されたオプションで実行されます。sto3g基底をに使用すると、22電子を持つ19個の空間軌道があります。HiVQE計算で(10o,10e)ケースを実行するために、10個の活性軌道と6個の凍結軌道を定義できます。各反復において、circularエンタングルメントと2回の繰り返し(reps)を持つExcitationPreserving量子回路(epa)によって生成された電子配置をサンプリングするために100ショットが使用されます。エネルギー収束による反復の終了を保証するため、最大反復回数は30に設定されています。
molecule_options = {
"basis": "sto3g",
"active_orbitals": list(range(5, 15)),
"frozen_orbitals": list(range(5)),
}
hivqe_options = {
"shots": 100,
"max_iter": 30,
"ansatz": "epa",
"ansatz_entanglement": "circular",
"ansatz_reps": 2,
}
ステップ2および3:量子ハードウェア実行のための問題の最適化とHiVQE Chemistry関数を用いた実行
以下に定義されたオプションでジオメトリに対するHiVQE計算を実行するためのforループを設定します。ジョブはforループ内で送信されます。このチュートリアルでは、6つのジオメトリを送信し、すべてが完了した時点で結果を取得します。メインの関数実行では、max_statesとmax_expansion_statesを定義して、部分空間行列の最大サイズと、反復ごとに古典的なCI展開法を使用して生成できる状態数を制御する必要があります。関数のジョブIDは、出力の追跡と処理のために各ジオメトリのラベルとともに辞書に格納されます。
info_jobid = {}
for dis, geom in str_geometries.items():
hivqe_run = hivqe.run(
geometry=geom,
backend_name="",
max_states=40000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
status = hivqe_run.status()
info_jobid[dis] = hivqe_run.job_id
print(info_jobid)
{'1.51': 'de3b8818-c9db-4fa3-a3c2-d51551c2dfaf', '1.91': '55d9467a-fc85-49a8-9bc6-8f6990e421e5', '2.40': '415112b3-69ff-4d53-8b10-cb4e3be68c9e', '3.10': 'ef67b600-3887-4225-b872-e354dfdf8454', '3.80': 'b16d3502-a9e4-4560-9775-852e9d07e70f', '4.50': '0c0bffc7-af77-4a56-a656-2a2610c991d6'}
すべてのジョブがまだ実行中か、完了しているかを確認しましょう。
completed_jobs_num = 0
running_jobs_num = 0
completed_jobs = {}
for i, info in enumerate(info_jobid.items()):
dis, job_id = info
submitted_job = catalog.get_job_by_id(job_id)
stat = submitted_job.status()
print(dis, submitted_job.job_id, stat)
if stat == "DONE":
completed_jobs_num += 1
completed_jobs[dis] = submitted_job
if (stat == "RUNNING") or (stat == "QUEUED"):
running_jobs_num += 1
print(
f"Completed {completed_jobs_num} job, Running or Queued {running_jobs_num} job"
)
1.51 de3b8818-c9db-4fa3-a3c2-d51551c2dfaf DONE
1.91 55d9467a-fc85-49a8-9bc6-8f6990e421e5 DONE
2.40 415112b3-69ff-4d53-8b10-cb4e3be68c9e DONE
3.10 ef67b600-3887-4225-b872-e354dfdf8454 DONE
3.80 b16d3502-a9e4-4560-9775-852e9d07e70f DONE
4.50 0c0bffc7-af77-4a56-a656-2a2610c991d6 DONE
Completed 6 job, Running or Queued 0 job
すべてのジョブが完了したら、すべての計算結果を取得しましょう。
hivqe_result = {}
if len(info_jobid) == completed_jobs_num:
print("All jobs are completed")
for i, job in enumerate(completed_jobs.items()):
dis, cal = job
print(dis, cal.result()["energy"])
hivqe_result[str(dis)] = cal.result()["energy"]
All jobs are completed
1.51 -407.8944801731773
1.91 -407.9800570932916
2.40 -407.9372992999806
3.10 -407.86278336000134
3.80 -407.83092972296157
4.50 -407.82971011225766
pprint.pprint(hivqe_result)
{'1.51': -407.8944801731773,
'1.91': -407.9800570932916,
'2.40': -407.9372992999806,
'3.10': -407.86278336000134,
'3.80': -407.83092972296157,
'4.50': -407.82971011225766}
ジョブで使用されたQPU実行時間の全体は、IBM Quantum Platformにログインし、qunova-chemistry-hivqeタグで送信されたジョブを表示することで追跡できます。
ステップ4:後処理と古典的手法との比較
HiVQEの結果を検証するために、(10o,10e)に対する古典的な参照計算(CASCI)を実行できます。
str_geometries = {
"1.31": "S -1.250686 0.660708 -0.095168; Li -1.482812 0.453464 -1.369406; Li -0.911870 0.962810 1.762020",
"1.41": "S -1.244856 0.665971 -0.062773; Li -1.494574 0.442933 -1.434177; Li -0.905937 0.968078 1.794395",
"1.51": "S -1.239044 0.671232 -0.030374; Li -1.506327 0.432403 -1.498949; Li -0.899996 0.973348 1.826768",
"1.61": "S -1.233245 0.676492 0.002027; Li -1.518073 0.421873 -1.563722; Li -0.894049 0.978617 1.859141",
"1.71": "S -1.227453 0.681752 0.034429; Li -1.529816 0.411343 -1.628496; Li -0.888099 0.983887 1.891513",
"1.81": "S -1.221659 0.687012 0.066831; Li -1.541558 0.400813 -1.693270; Li -0.882150 0.989157 1.923885",
"1.91": "S -1.215858 0.692272 0.099232; Li -1.553305 0.390283 -1.758043; Li -0.876205 0.994426 1.956257",
"2.01": "S -1.209887 0.697544 0.131599; Li -1.565136 0.379748 -1.822800; Li -0.870344 0.999691 1.988646",
"2.11": "S -1.203945 0.702813 0.163973; Li -1.576953 0.369214 -1.887560; Li -0.864469 1.004956 2.021033",
"2.21": "S -1.198023 0.708081 0.196350; Li -1.588760 0.358680 -1.952322; Li -0.858584 1.010221 2.053417",
"2.30": "S -1.365426 0.717714 0.367060; Li -0.689401 0.458925 -1.828368; Li -1.500219 0.981173 2.255876",
"2.31": "S -1.192118 0.713348 0.228731; Li -1.600559 0.348146 -2.017085; Li -0.852690 1.015488 2.085800",
"2.40": "S -1.741432 0.680397 0.346702; Li -0.529307 0.488006 -1.729343; Li -1.284307 0.989409 2.177209",
"2.50": "S -1.885961 0.669986 0.365815; Li -0.461563 0.499084 -1.695846; Li -1.207523 0.988741 2.124599",
"2.60": "S -1.977163 0.665155 0.389784; Li -0.416654 0.504966 -1.683655; Li -1.161229 0.987690 2.088439",
"2.70": "S -2.063642 0.661518 0.418977; Li -0.367600 0.510505 -1.676408; Li -1.123804 0.985788 2.051998",
"2.80": "S -2.141072 0.659218 0.451663; Li -0.323153 0.515056 -1.673046; Li -1.090821 0.983538 2.015951",
"2.90": "S -2.212097 0.657968 0.487535; Li -0.281989 0.518909 -1.672407; Li -1.060960 0.980935 1.979440",
"3.00": "S -2.281477 0.657123 0.525155; Li -0.239607 0.523326 -1.668669; Li -1.033963 0.977363 1.938081",
"3.10": "S -2.347450 0.657089 0.566194; Li -0.199353 0.527517 -1.665148; Li -1.008243 0.973206 1.893522",
"3.20": "S -2.410882 0.657532 0.608912; Li -0.157788 0.532069 -1.659971; Li -0.986376 0.968211 1.845627",
"3.30": "S -2.470306 0.658818 0.654893; Li -0.118007 0.536237 -1.656311; Li -0.966733 0.962757 1.795986",
"3.40": "S -2.525776 0.660762 0.702910; Li -0.078312 0.540189 -1.654076; Li -0.950958 0.956861 1.745734",
"3.50": "S -2.576885 0.663376 0.752788; Li -0.039076 0.543706 -1.654536; Li -0.939085 0.950730 1.696316",
"3.60": "S -2.623930 0.666534 0.803853; Li 0.000274 0.546839 -1.657697; Li -0.931390 0.944439 1.648412",
"3.70": "S -2.667364 0.670217 0.856250; Li 0.039572 0.549616 -1.663265; Li -0.927254 0.937980 1.601583",
"3.80": "S -2.707255 0.674298 0.909161; Li 0.079218 0.552012 -1.671656; Li -0.927010 0.931502 1.557063",
"3.90": "S -2.744005 0.678718 0.962425; Li 0.119268 0.554073 -1.682595; Li -0.930310 0.925021 1.514738",
"4.00": "S -2.777891 0.683415 1.015798; Li 0.159751 0.555810 -1.696024; Li -0.936907 0.918587 1.474794",
"4.10": "S -2.809179 0.688333 1.069057; Li 0.200678 0.557234 -1.711873; Li -0.946546 0.912245 1.437385",
"4.20": "S -2.838194 0.693443 1.122205; Li 0.242066 0.558401 -1.729770; Li -0.958918 0.905968 1.402134",
"4.30": "S -2.864984 0.698619 1.174415; Li 0.283858 0.559186 -1.750539; Li -0.973920 0.900007 1.370693",
"4.40": "S -2.889984 0.703887 1.226140; Li 0.326068 0.559728 -1.773231; Li -0.991131 0.894196 1.341660",
"4.50": "S -2.913363 0.709175 1.276987; Li 0.368656 0.559989 -1.798088; Li -1.010340 0.888647 1.315670",
}
rhf_result = {}
casci_result = {}
cas_list = molecule_options["active_orbitals"]
distance_ref = []
for dis, geom in str_geometries.items():
distance_ref.append(dis)
mole = gto.M(atom=geom, basis=molecule_options["basis"])
mole.verbose = 0
# RHF energy
mf = scf.RHF(mole).run()
mo_occ = mf.mo_occ
num_elecs_as = int(sum([mo_occ[idx] for idx in cas_list]))
rhf_result[str(dis)] = mf.e_tot
# CASCI energy
casci_solver = mcscf.CASCI(mf, len(cas_list), num_elecs_as)
orbs = mcscf.addons.sort_mo(casci_solver, mf.mo_coeff, cas_list, base=0)
casci_solver.kernel(orbs)
casci_result[str(dis)] = casci_solver.e_tot
print(
f"d={dis:4.3} RHF Energy: {mf.e_tot:14.10}, CASCI Energy: {casci_solver.e_tot:14.10}"
)
d=1.3 RHF Energy: -407.7137006, CASCI Energy: -407.7193917
d=1.4 RHF Energy: -407.8183196, CASCI Energy: -407.8245211
d=1.5 RHF Energy: -407.8878013, CASCI Energy: -407.8944802
d=1.6 RHF Energy: -407.9315356, CASCI Energy: -407.9385663
d=1.7 RHF Energy: -407.9569034, CASCI Energy: -407.9641258
d=1.8 RHF Energy: -407.9693681, CASCI Energy: -407.9766313
d=1.9 RHF Energy: -407.9728592, CASCI Energy: -407.9800572
d=2.0 RHF Energy: -407.9701684, CASCI Energy: -407.9772549
d=2.1 RHF Energy: -407.9632701, CASCI Energy: -407.9702381
d=2.2 RHF Energy: -407.9535584, CASCI Energy: -407.9604007
d=2.3 RHF Energy: -407.9420173, CASCI Energy: -407.9487043
d=2.3 RHF Energy: -407.9420156, CASCI Energy: -407.9487024
d=2.4 RHF Energy: -407.9297216, CASCI Energy: -407.9372993
d=2.5 RHF Energy: -407.9172, CASCI Energy: -407.9261859
d=2.6 RHF Energy: -407.9061139, CASCI Energy: -407.915961
d=2.7 RHF Energy: -407.8937118, CASCI Energy: -407.904259
d=2.8 RHF Energy: -407.8816389, CASCI Energy: -407.8928292
d=2.9 RHF Energy: -407.8700448, CASCI Energy: -407.8819574
d=3.0 RHF Energy: -407.859054, CASCI Energy: -407.8719092
d=3.1 RHF Energy: -407.8487619, CASCI Energy: -407.8628304
d=3.2 RHF Energy: -407.8392304, CASCI Energy: -407.8548482
d=3.3 RHF Energy: -407.8304842, CASCI Energy: -407.8480217
d=3.4 RHF Energy: -407.8225124, CASCI Energy: -407.8423743
d=3.5 RHF Energy: -407.8152758, CASCI Energy: -407.8378892
d=3.6 RHF Energy: -407.8087161, CASCI Energy: -407.8345331
d=3.7 RHF Energy: -407.802764, CASCI Energy: -407.8322563
d=3.8 RHF Energy: -407.7973458, CASCI Energy: -407.83093
d=3.9 RHF Energy: -407.7923883, CASCI Energy: -407.8303555
d=4.0 RHF Energy: -407.7878216, CASCI Energy: -407.83025
d=4.1 RHF Energy: -407.783582, CASCI Energy: -407.8303243
d=4.2 RHF Energy: -407.7796124, CASCI Energy: -407.8303791
d=4.3 RHF Energy: -407.7758633, CASCI Energy: -407.8302885
d=4.4 RHF Energy: -407.7722923, CASCI Energy: -407.8300614
d=4.5 RHF Energy: -407.7688641, CASCI Energy: -407.829711
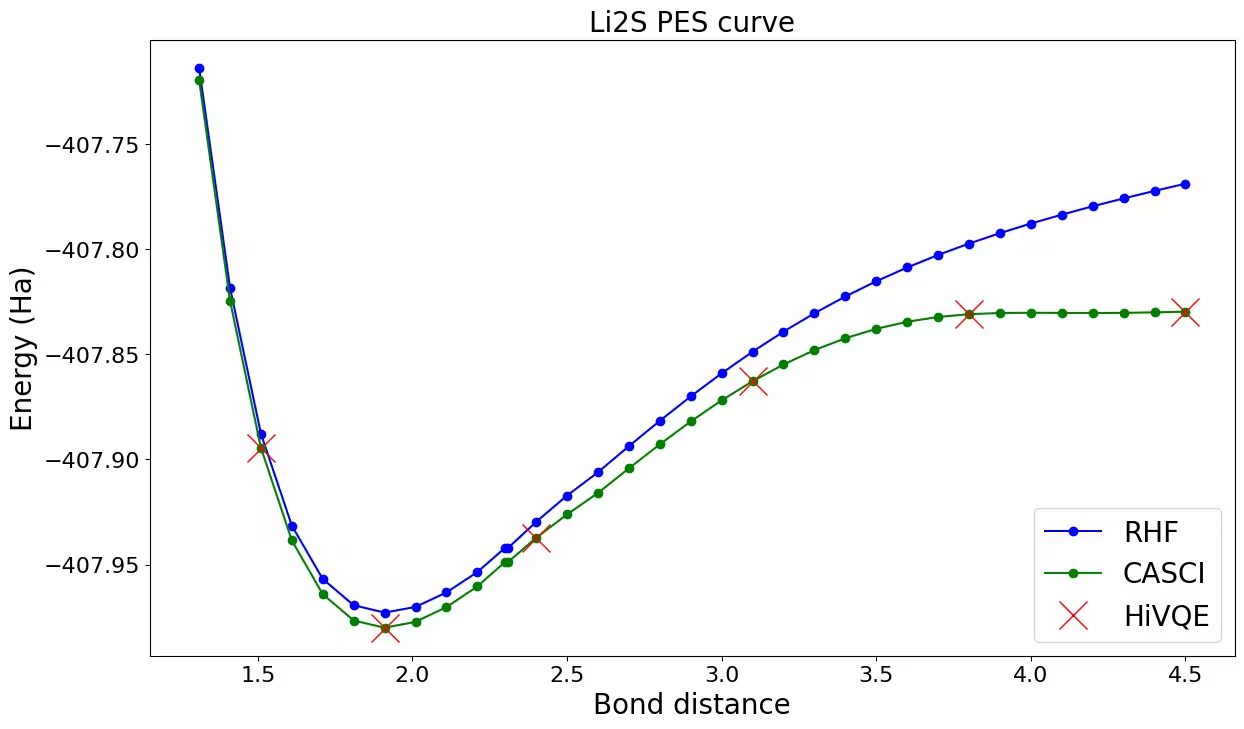
Li_2Sの解離曲線のプロット
HiVQEの結果をHFおよびCASCIと比較してプロットしましょう。 すべてのHiVQE計算が古典的な参照結果(CASCI)と良く一致していることが確認できます。
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Bond distance (angstrom)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("Li2S PES curve", size=20)
fig.set_size_inches(14, 8)
パート 2: FeP-NO (44Q)
ステップ 1: 古典的な入力を量子問題にマッピングする
HiVQE 計算のオプションを定義します。
molecule_options = {
"basis": "631g*",
"active_orbitals": list(range(90, 112, 1)),
"frozen_orbitals": list(range(0, 90, 1)),
"charge": -1,
}
hivqe_options = {
"shots": 2000,
"max_iter": 40,
"ansatz": "epa",
"ansatz_entanglement": "linear",
"ansatz_reps": 2,
"amplitude_screening_tolerance": 1e-6,
}
PES 曲線を計算するために、Fe-N の異なる結合距離に対する FeP-NO の分子構造を辞書形式で定義します。
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
geometry_1_75 = """
Fe 9.910596 31.534095 1.798088
N 10.557481 31.888419 -0.055204
N 11.823496 31.255002 2.384659
N 9.292831 30.783362 3.568730
N 8.036805 31.418327 1.124265
C 9.784765 32.177349 -1.158798
C 10.612656 32.501029 -2.296868
C 11.903375 32.404043 -1.876832
C 11.859093 32.028943 -0.483750
C 12.965737 31.464698 1.641427
C 14.146517 31.236323 2.440231
C 13.713061 30.885870 3.681911
C 12.268752 30.896411 3.634891
C 10.067717 30.486167 4.664747
C 9.246224 30.053411 5.772052
C 7.957075 30.082846 5.336488
C 7.995710 30.538421 3.967046
C 6.900258 31.104497 1.836595
C 5.722470 31.251707 1.015333
C 6.148430 31.668586 -0.207993
C 7.587039 31.767438 -0.130483
C 8.399453 32.134197 -1.192329
H 7.912872 32.388031 -2.131079
C 12.984883 31.836053 0.306093
H 13.955948 31.977044 -0.162626
C 11.453768 30.560663 4.708020
H 11.940677 30.298823 5.644352
C 6.877071 30.697580 3.164102
H 5.907240 30.476797 3.603674
H 12.813946 32.569160 -2.441577
H 10.236332 32.758110 -3.280309
H 15.164312 31.335191 2.080201
H 14.299625 30.629109 4.556760
H 9.626524 29.758225 6.743433
H 7.053076 29.823583 5.875809
H 4.709768 31.058315 1.350561
H 5.561898 31.886355 -1.093106
N 9.832739 33.209042 2.298783
O 9.346337 34.075996 1.606023
"""
geometry_2_00 = """
Fe 9.917990 31.445558 1.778346
N 10.556809 31.866188 -0.055498
N 11.814089 31.227003 2.372666
N 9.297875 30.758246 3.550104
N 8.043584 31.397768 1.120485
C 9.784831 32.164652 -1.160219
C 10.611624 32.501801 -2.293514
C 11.902858 32.406547 -1.875160
C 11.859552 32.017818 -0.486307
C 12.960503 31.454432 1.636717
C 14.140770 31.242960 2.439615
C 13.708543 30.884151 3.678983
C 12.266351 30.874173 3.627468
C 10.070264 30.465070 4.655102
C 9.247247 30.053101 5.766681
C 7.958085 30.091201 5.332866
C 7.998432 30.529979 3.958727
C 6.901428 31.093932 1.833807
C 5.723289 31.255057 1.016540
C 6.151314 31.670649 -0.206350
C 7.589736 31.755538 -0.133074
C 8.400230 32.124963 -1.194447
H 7.913264 32.386655 -2.130914
C 12.983905 31.827747 0.302415
H 13.955696 31.979687 -0.161365
C 11.454251 30.533644 4.698234
H 11.941002 30.276716 5.636156
C 6.877444 30.689985 3.159940
H 5.907605 30.480118 3.604825
H 12.813105 32.581608 -2.437367
H 10.233725 32.768337 -3.273979
H 15.157796 31.357524 2.082132
H 14.295001 30.638320 4.557047
H 9.626721 29.768762 6.741623
H 7.051752 29.847502 5.875478
H 4.709710 31.071712 1.354640
H 5.565103 31.898376 -1.089333
N 9.840508 33.353531 2.373019
O 9.344561 34.158205 1.637232
"""
geometry_5_00 = """
Fe 9.918629 31.289202 1.717339
N 10.542914 31.832173 -0.080685
N 11.795572 31.199413 2.341831
N 9.294593 30.741247 3.513929
N 8.042689 31.359481 1.087282
C 9.775254 32.111817 -1.200449
C 10.600219 32.479101 -2.319680
C 11.891090 32.425876 -1.887580
C 11.847694 32.024341 -0.507342
C 12.945734 31.464689 1.611366
C 14.116395 31.289997 2.423572
C 13.685777 30.915122 3.663719
C 12.252381 30.861042 3.608186
C 10.062170 30.463021 4.634102
C 9.236749 30.104333 5.755782
C 7.945687 30.161198 5.324720
C 7.989641 30.552269 3.941498
C 6.892881 31.087489 1.815829
C 5.722676 31.253502 1.001149
C 6.153153 31.631057 -0.238233
C 7.586010 31.695401 -0.179773
C 8.390724 32.047572 -1.247553
H 7.903308 32.291586 -2.187969
C 12.973334 31.849872 0.283741
H 13.944682 32.031190 -0.169145
C 11.447158 30.518591 4.678739
H 11.934423 30.277429 5.619969
C 6.864795 30.711643 3.146118
H 5.893357 30.532078 3.599511
H 12.800139 32.636412 -2.439296
H 10.224017 32.743662 -3.301293
H 15.131785 31.441247 2.076257
H 14.273933 30.694315 4.546802
H 9.612512 29.848040 6.739754
H 7.036117 29.960530 5.879248
H 4.707408 31.099933 1.347803
H 5.564992 31.851940 -1.121294
N 9.666041 36.091609 3.085945
O 9.598728 37.226756 3.411299
"""
str_geometries = {
"1.75": geometry_1_75,
"2.00": geometry_2_00,
"5.00": geometry_5_00,
}
hivqe_result = {}
{'5.0': '\nFe 9.918629 31.289202 1.717339\nN 10.542914 31.832173 -0.080685\nN 11.795572 31.199413 2.341831\nN 9.294593 30.741247 3.513929\nN 8.042689 31.359481 1.087282\nC 9.775254 32.111817 -1.200449\nC 10.600219 32.479101 -2.319680\nC 11.891090 32.425876 -1.887580\nC 11.847694 32.024341 -0.507342\nC 12.945734 31.464689 1.611366\nC 14.116395 31.289997 2.423572\nC 13.685777 30.915122 3.663719\nC 12.252381 30.861042 3.608186\nC 10.062170 30.463021 4.634102\nC 9.236749 30.104333 5.755782\nC 7.945687 30.161198 5.324720\nC 7.989641 30.552269 3.941498\nC 6.892881 31.087489 1.815829\nC 5.722676 31.253502 1.001149\nC 6.153153 31.631057 -0.238233\nC 7.586010 31.695401 -0.179773\nC 8.390724 32.047572 -1.247553\nH 7.903308 32.291586 -2.187969\nC 12.973334 31.849872 0.283741\nH 13.944682 32.031190 -0.169145\nC 11.447158 30.518591 4.678739\nH 11.934423 30.277429 5.619969\nC 6.864795 30.711643 3.146118\nH 5.893357 30.532078 3.599511\nH 12.800139 32.636412 -2.439296\nH 10.224017 32.743662 -3.301293\nH 15.131785 31.441247 2.076257\nH 14.273933 30.694315 4.546802\nH 9.612512 29.848040 6.739754\nH 7.036117 29.960530 5.879248\nH 4.707408 31.099933 1.347803\nH 5.564992 31.851940 -1.121294\nN 9.666041 36.091609 3.085945\nO 9.598728 37.226756 3.411299\n'}
ステップ 2 および 3: 量子ハードウェア実行のための問題の最適化と HiVQE Chemistry 関数を使用した実行
HiVQE の設定と分子構造に基づいて、結果を順次取得します。
d(Fe-N) = 1.75 の計算を送信します。
hivqe_run_1_75 = hivqe.run(
geometry=str_geometries["1.75"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_1_75 = hivqe_run_1_75.job_id
d(Fe-N) = 1.75 の計算のジョブを追跡し、結果を取得します。
submitted_job_1_75 = catalog.get_job_by_id(info_jobid_1_75)
stat = submitted_job_1_75.status()
print(submitted_job_1_75.job_id, stat)
if stat == "DONE":
hivqe_run_1_75_energy = submitted_job_1_75.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_1_75_energy}")
hivqe_result["1.75"] = hivqe_run_1_75_energy
d(Fe-N) = 2.00 の計算を送信します。
hivqe_run_2_00 = hivqe.run(
geometry=str_geometries["2.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_2_00 = hivqe_run_2_00.job_id
d(Fe-N) = 2.00 の計算のジョブを追跡し、結果を取得します。
submitted_job_2_00 = catalog.get_job_by_id(info_jobid_2_00)
stat = submitted_job_2_00.status()
print(submitted_job_2_00.job_id, stat)
if stat == "DONE":
hivqe_run_2_00_energy = submitted_job_2_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_2_00_energy}")
hivqe_result["2.00"] = hivqe_run_2_00_energy
d(Fe-N) = 5.00 の計算を送信します。
hivqe_run_5_00 = hivqe.run(
geometry=str_geometries["5.00"],
backend_name="",
max_states=400000000,
max_expansion_states=100,
molecule_options=molecule_options,
hivqe_options=hivqe_options,
)
info_jobid_5_00 = hivqe_run_5_00.job_id
d(Fe-N) = 5.00 の計算のジョブを追跡し、結果を取得します。
submitted_job_5_00 = catalog.get_job_by_id(info_jobid_5_00)
stat = submitted_job_5_00.status()
print(submitted_job_5_00.job_id, stat)
if stat == "DONE":
hivqe_run_5_00_energy = submitted_job_5_00.result()["energy"]
print(f"Completed HiVQE calculation, Energy {hivqe_run_5_00_energy}")
hivqe_result["5.00"] = hivqe_run_5_00_energy
hivqe_result = {
"1.75": -2373.681781,
"2.00": -2373.694128,
"5.00": -2373.637807,
}
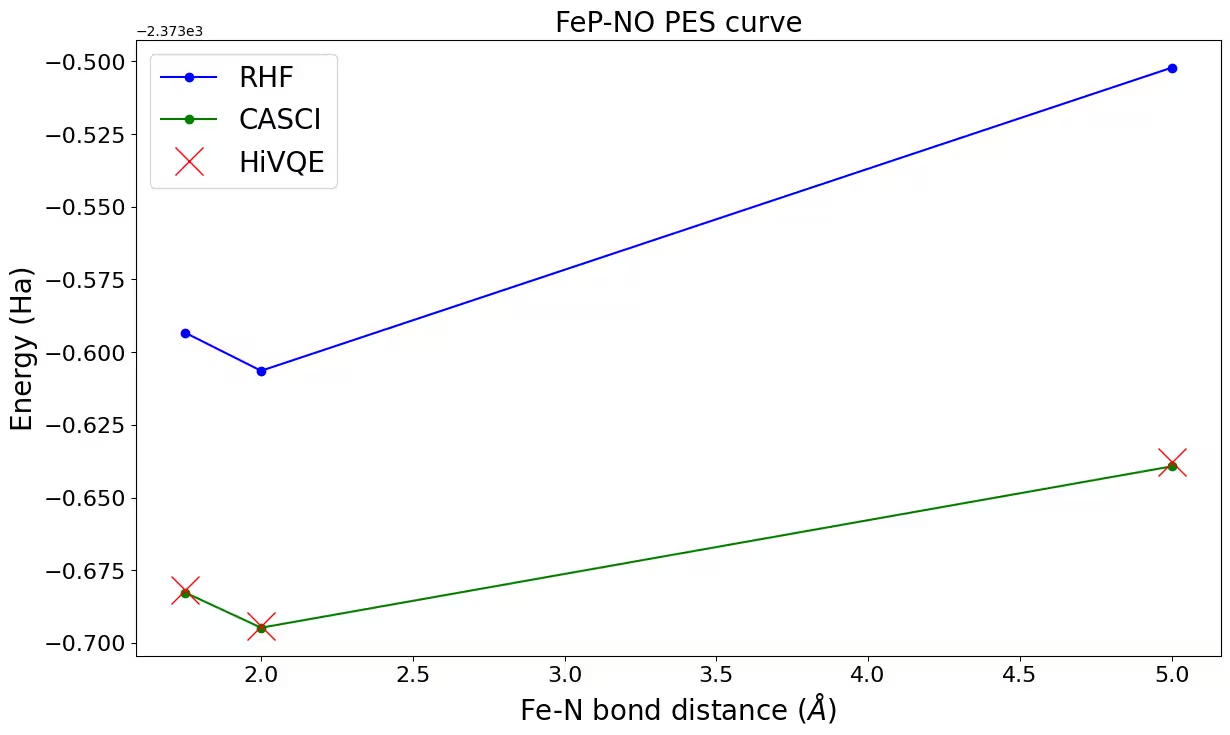
ステップ 4: 後処理と古典的手法との比較
HiVQE の結果を検証するために、(22o,22e) に対する古典的な参照計算(CASCI-DMRG、maxM=800)の結果を以下に示します。
rhf_result = {
"1.75": -2373.59331683504,
"2.00": -2373.60640773065,
"5.00": -2373.50214278007,
}
casci_result = {"1.75": -2373.6827, "2.00": -2373.6948, "5.00": -2373.6393}
fig, ax = plt.subplots(1, 1)
hf_energy = [v for key, v in rhf_result.items()]
casci_energy = [v for key, v in casci_result.items()]
hivqe_energy = [v for key, v in hivqe_result.items()]
distance_ref = [float(key) for key, v in rhf_result.items()]
distance = [float(key) for key, v in hivqe_result.items()]
ax.plot(distance_ref, hf_energy, "-o", label="RHF", c="blue")
ax.plot(distance_ref, casci_energy, "-o", label="CASCI", c="green")
ax.plot(distance, hivqe_energy, "x", label="HiVQE", c="red", markersize=20)
ax.legend(fontsize=20)
ax.tick_params("both", labelsize=16)
ax.set_xlabel("Fe-N bond distance ($\AA$)", size=20)
ax.set_ylabel("Energy (Ha)", size=20)
ax.set_title("FeP-NO PES curve", size=20)
fig.set_size_inches(14, 8)
チュートリアルアンケート
このチュートリアルに関するフィードバックをお寄せいただくため、短いアンケートにご協力ください。皆様のご意見は、コンテンツの改善とユーザー体験の向上に役立てさせていただきます。
Note: This survey is provided by IBM Quantum and relates to the original English content. To give feedback on doQumentation's website, translations, or code execution, please open a GitHub issue.